🧐 Slingshot | 细胞分化轨迹的这样做比较简单哦!~(二)
导读:1写在前面今天又值班了,你没有听错!!🥲又值班了!!!!😅最近自己的确不太在状态,做事情有极强的拖延症,要振奋起来啦,man!~😣BTW,大家最近有没有什么好听的歌推荐推荐啊,曲荒了!~😭好吧,今天的教程接上次的继续,依然是slingsho...
1写在前面
今天又值班了,你没有听错!!🥲
又值班了!!!!😅
最近自己的确不太在状态,做事情有极强的拖延症,要振奋起来啦,man!~😣
BTW,大家最近有没有什么好听的歌推荐推荐啊,曲荒了!~😭
好吧,今天的教程接上次的继续,依然是slingshot。🤪
上次有小伙伴问做这个分析有什么用???🤨
好吧,比如说你做了PCA发现有2群细胞差异还挺明显的,但是用FindMarkers就是找不到差异基因。🥲
可能这2群是同一群细胞,只是处于不同的分化状态而已,两者之间并没有明显的差异。🧐
However,两者之间存在一个平滑的过渡,通过逐渐的转录组变化来改变细胞状态。😏
所以做分化轨迹分析可以了解细胞是如何改变细胞状态以及细胞命运的决定机制。😚
2用到的包
rm(list = ls())
library(slingshot)
library(tidyverse)
library(uwot)
library(mclust)
library(RColorBrewer)
library(grDevices)
3示例数据
data("slingshotExample")
rd - slingshotExample$rd
cl - slingshotExample$cl
dim(rd)
length(cl)

4构建PseudotimeOrdering
这里我们要用到示例二了,这里我们直接使用降维文件和聚类文件进行构建咯。🤒
lin1 - getLineages(rd, cl, start.clus = '1')
lin1
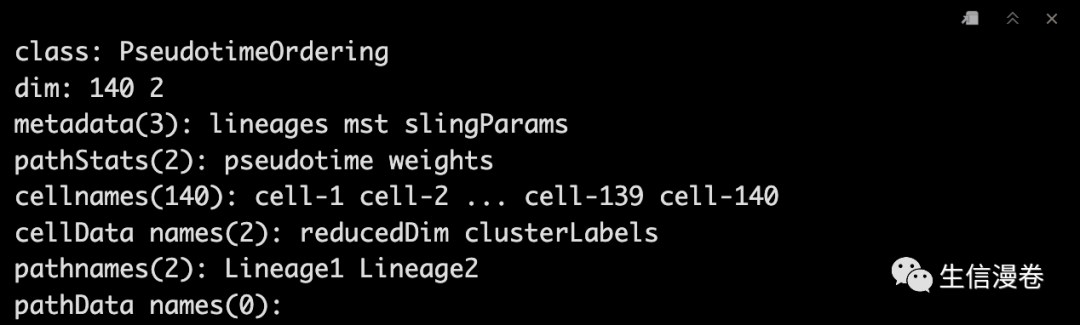
5可视化
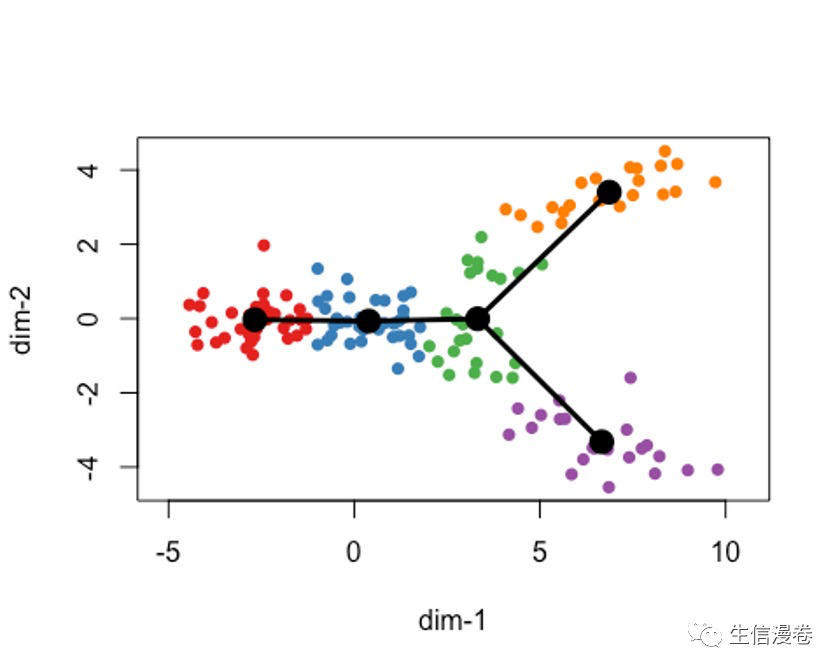
plot(rd, col = brewer.pal(9,"Set1")[cl], asp = 1, pch = 16)
lines(SlingshotDataSet(lin1), lwd = 3, col = 'black')
6指定cluster为endpoint
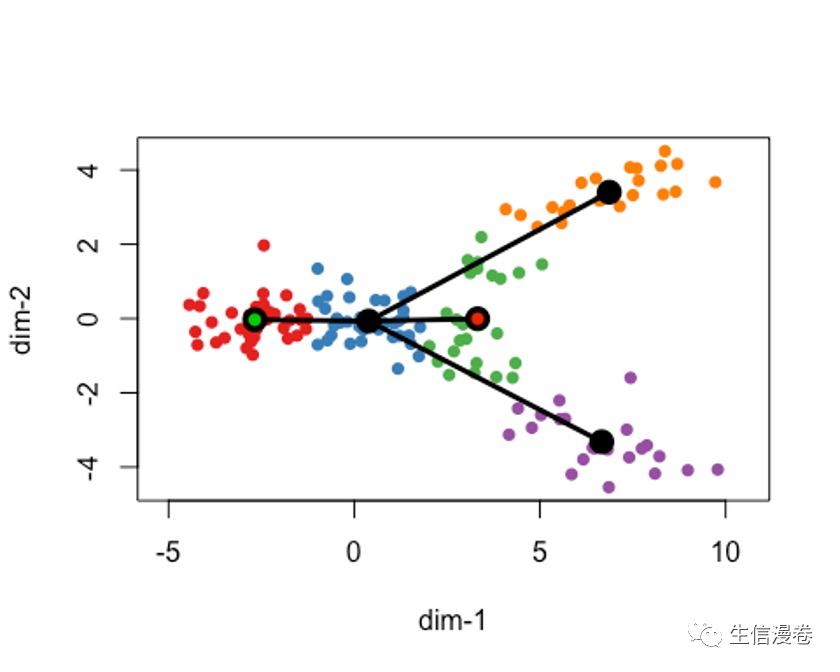
这里我们制定Cluster 3作为endpoint。🧐
这样做是有一定的好处的,可以防止已知的细胞阶段被归类为瞬时状态。😬
lin2 - getLineages(rd, cl, start.clus= '1', end.clus = '3')
plot(rd, col = brewer.pal(9,"Set1")[cl], asp = 1, pch = 16)
lines(SlingshotDataSet(lin2), lwd = 3, col = 'black', show.constraints = T)
7创建平滑曲线
crv1 - getCurves(lin1)
crv1
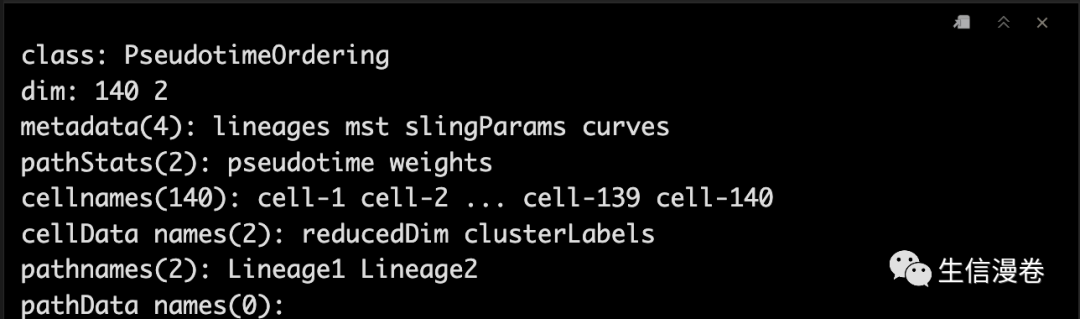
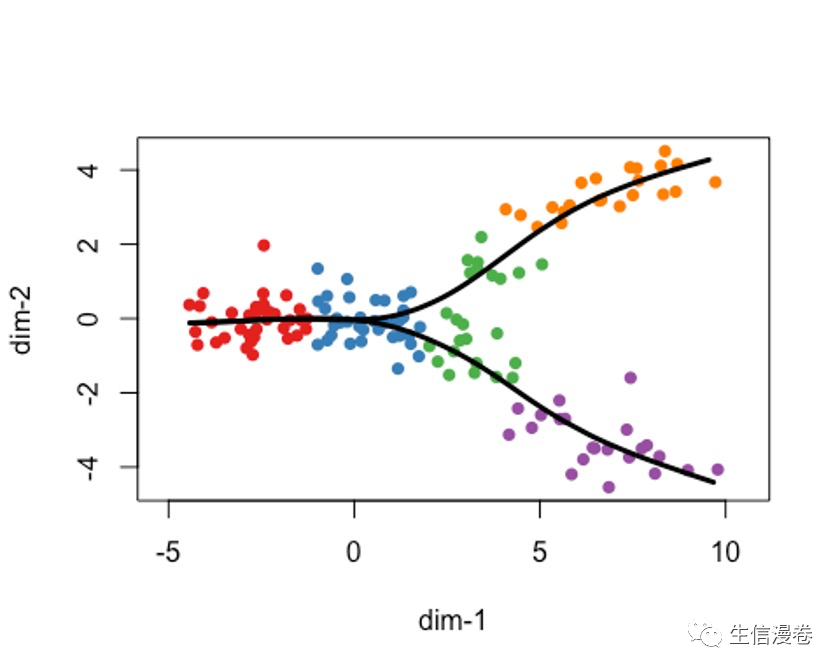
8可视化
plot(rd, col = brewer.pal(9,"Set1")[cl], asp = 1, pch = 16)
lines(SlingshotDataSet(crv1), lwd = 3, col = 'black')
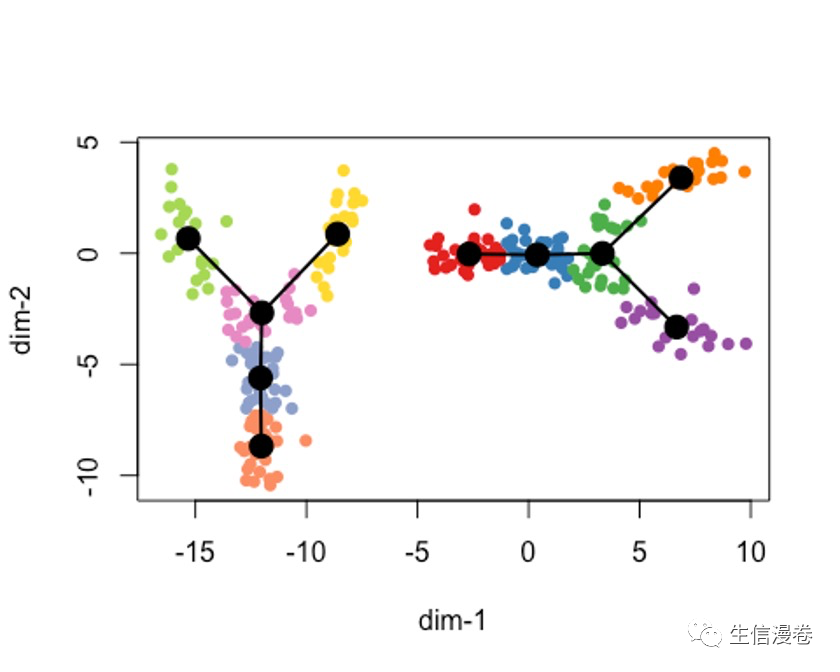
9多轨迹的处理
这里的话我们要设置omega = TRUE。🥰
rd2 - rbind(rd, cbind(rd[,2]-12, rd[,1]-6))
cl2 - c(cl, cl + 10)
pto2 - slingshot(rd2, cl2, omega = T, start.clus = c(1,11))
plot(rd2, pch=16, asp = 1,
col = c(brewer.pal(9,"Set1"), brewer.pal(8,"Set2"))[cl2])
lines(SlingshotDataSet(pto2), type = 'l', lwd=2, col='black')
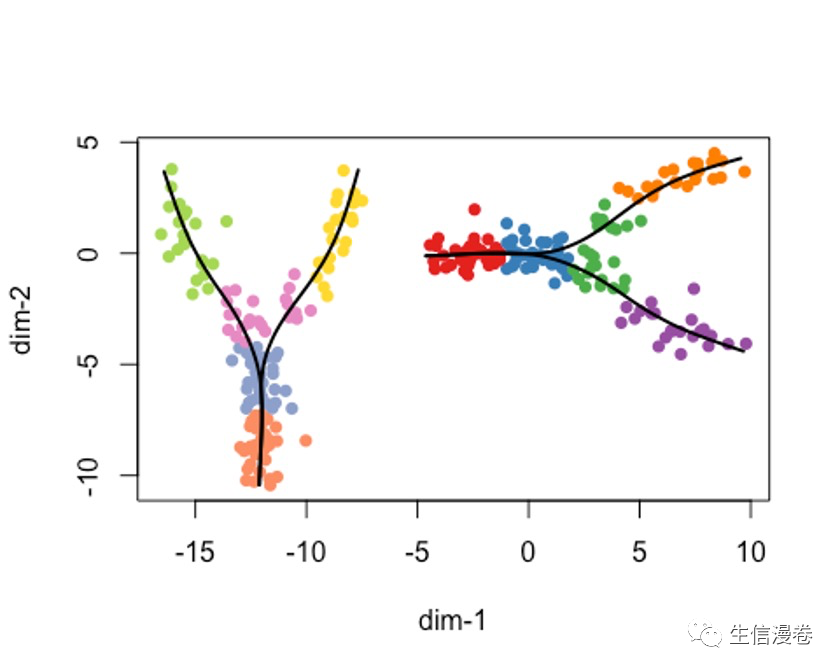
拟合完之后,再分别处理每个trajectory,拟合主线。😂
plot(rd2, pch=16, asp = 1,
col = c(brewer.pal(9,"Set1"), brewer.pal(8,"Set2"))[cl2])
lines(SlingshotDataSet(pto2), lwd=2, col='black')
声明:本文内容由网友自发贡献,本站不承担相应法律责任。对本内容有异议或投诉,请联系2913721942#qq.com核实处理,我们将尽快回复您,谢谢合作!
若转载请注明出处: 🧐 Slingshot | 细胞分化轨迹的这样做比较简单哦!~(二)
本文地址: https://pptw.com/jishu/557838.html
